Das Team von Professor Stein Aerts von VIB-KU Leuven in Belgien hat kürzlich in der Fachzeitschrift „Nature Methods“ eine neue Studie veröffentlicht, die ein Softwarepaket namens CREsted vorstellt. Dieses soll genetische Regulatoren auf systematische und skalierbare Weise analysieren und entwerfen. Das Werkzeug adressiert die Anwendungsherausforderungen, denen KI bei der Entschlüsselung der DNA-Regulationslogik gegenübersteht, insbesondere im Hinblick auf verschiedene Datensätze, Gewebe und Spezies.
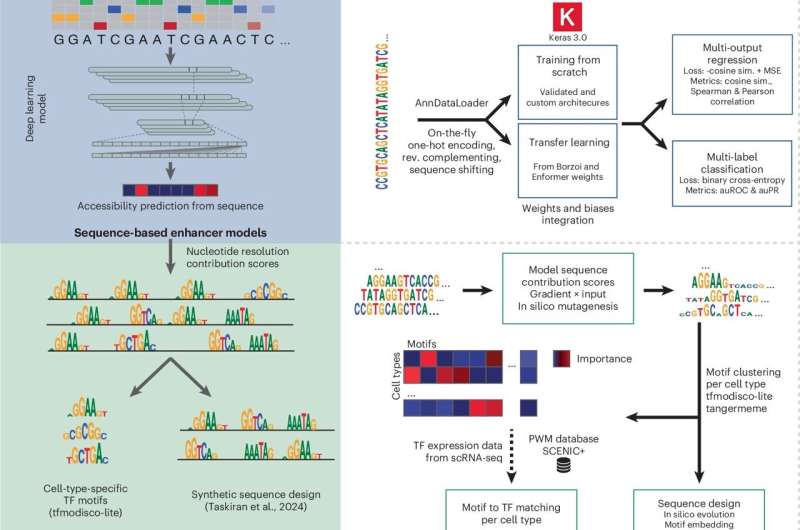
Genetische Regulatoren wie Enhancer sind kurze DNA-Sequenzen, die die Genaktivität steuern, aber bestehende Methoden sind oft auf einzelne Datensätze beschränkt und schwer wiederzuverwenden oder zu erweitern. Das CREsted-Framework wandelt die Modellierung von Enhancern von einer einmaligen Analyse in einen systematischeren Arbeitsablauf um. Es integriert Schritte wie Vorverarbeitung, Modelltraining, Interpretation und den Entwurf synthetischer Enhancer und passt sich an Einzelzell-Analyseprozesse an, um die Übernahme durch Forscher zu erleichtern.
„Wir wollten über Einmalmodelle hinausgehen“, sagte Niklas Kempynck, Doktorand im Aerts-Labor. „CREsted ermöglicht es Forschern, die Enhancer-Logik in biologischen Systemen systematisch zu untersuchen, beginnend mit Zell-für-Zell-Atlanten zugänglicher regulatorischer DNA bis hin zum Sequenzdesign.“ Dr. Seppe De Winter, Co-Erstautor neben Kempynck, fügte hinzu: „Mit CREsted bieten wir Forschern einen kompletten Workflow. Man kann Deep-Learning-Modelle auf Chromatin-Zugänglichkeitsdaten trainieren, die regulatorischen Merkmale interpretieren, die sie erfassen, und dann diese Modelle nutzen, um neue DNA-Sequenzen mit vorhergesagter zelltypspezifischer Aktivität zu entwerfen.“
Das Team hat CREsted bereits auf mehrere Systeme angewandt, darunter Mäusegewebe, menschliche Immunzellen, Krebszellzustände und die Entwicklung von Zebrafischen. Dabei gelang es, regulatorische Muster zu identifizieren, Enhancer-Aktivität vorherzusagen und synthetische Enhancer zu entwerfen, die in Zebrafischen validiert wurden. Professor Stein Aerts, wissenschaftlicher Direktor von VIB.AI, sagte: „CREsted macht es einfacher, Enhancer-Modelle für verschiedene Datensätze zu trainieren, zu interpretieren und zu vergleichen. Das ist wichtig, wenn wir wollen, dass diese Methoden breit nutzbar werden – nicht nur für das Verständnis regulatorischer DNA, sondern auch für den systematischen Entwurf und Test neuer Sequenzen.“
Die Studie zeigt, wie KI das Feld der Genregulation von der Beschreibung hin zur Exploration und zum Design vorantreibt. Sie bietet ein systematischeres Werkzeug für die Erforschung genetischer Regulatoren mit Anwendungspotenzial in der Grundlagenbiologie, Biotechnologie und Medizin.
Veröffentlichungsdetails: Autor: VIB (das Flanders Institute for Biotechnology); Titel: „Software package makes gene regulation easier to study—and tweak“; Veröffentlicht in: „Nature Methods“ (2026); Zeitschrifteninfo: Nature Methods
